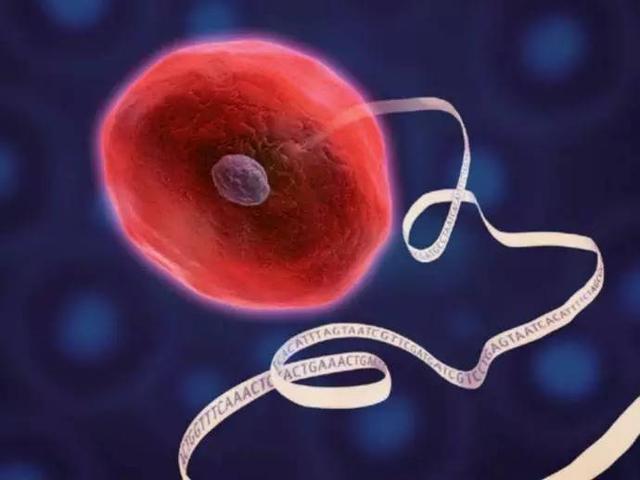
范文一:单细胞实验技术
一、单细胞裂解(3h )
1、 UP1引物定容到 0.5um :1ul 的UP1引物(100um )加入199ul 去核酸酶H2O 中,用小管盛装,并充分混匀;(所有的引物序列都列在表1) 2、准备细胞裂解液(4.45 ul每个样品),使用0.5ml 薄壁PCR 管,加入并混匀以下组分:
3、从输卵管获得四细胞时期胚胎,用口吸管转移到一滴台氏液(acidic Tyrode’s solution),以去除透明带;
关键步骤:在所有转移步骤中,在转移一个单细胞到裂解液前,需保证使用吸管时没有形成气泡。
4、将胚胎转移到无钙离子培养液中,轻轻吸动知道单个卵裂球分离出来; 5、随后将卵裂球转移到三个PBS-BSA 液滴中(50-100ul ),洗涤。
6、单个细胞被转移到含有4.45ul 新鲜准备的细胞裂解液中(用0.5ml 薄壁PCR 管)。先吸一小段PBS-BSA ,再吸细胞,然后全部打入裂解液中。
关键步骤:每个吸管只能用一次,不能重复利用,不能多次用于转移别的细胞到裂解液中。 关键步骤:应该有一个隐形对照样品,即没有细胞加入。
7、样品短暂离心:7500g ,30s ,4℃。然后立刻放置于冰上。 8、70℃孵育90s ,马上转移到冰上;
9、7500g ,30s ,4℃,然后立刻转移到冰上1min 。这个步骤之后,所有的mRNAs 将从单细胞中释放。
二、反转录(2h )
10、加入0.45ul RT mix(如下表)到每一个管中,从而每个RT 反应的体积达到5ul 每管:
12、逆转录酶失活,70℃,15min ;
13、离心7500g ,4℃,30s ,然后立刻转移到冰上1min 。这个步骤后,所有的mRNAs 的第一
条链cDNAs 合成。
三、自由引物去除(2h )
16、核酸外切酶失活:80℃,25min ;
17、离心7500g ,4℃,30s ,然后马上转移到冰上1min 。此步后,所有自由UP1引物被破坏,只保留了完整的5‘cDNA 末端;
四、3’Poly(A)加尾
18、准备TdT 反应混合物,如下表。每个反应加入6.0ul 混合物;
20、TdT 失活:70℃,10min ;
21、离心7500g
,4℃,30s ,然后马上转移到冰上1min 。此步后,第一链cDNAs3’末端加入了poly (A )尾;
五、第二链合成(1h )
24、每管中加入19ul PCR mix 1;
25、PCR 扩增:95℃,3min ;50℃,2min ;72℃,10min ;
26、冰浴1min ;
27、离心7500g ,4℃,30s ,然后马上转移到冰上。此步后,第二条链cDNAs 为5’-UP2-(T )
; n -UP1-3’
六、PCR 扩增
30、PCR 扩增:
首先95℃,3min ;
然后二十个循环:95℃,30s ;67℃,1min ;72℃,6min (每一个循环增加6s );4℃,保存。
此步后,所有的cDNAs 已经得到扩增。 将PCR 产物储存在-80℃(可保存6个月);或者转移到冰上,如果立刻继续进行第31步。
七、DNA 纯化
31、混匀每一管中的PCR 产物;
32、取10ul 混匀后的PCR 产物,加入90ulnuclease-free water,以稀释10倍。 取1ul 或2ul 这些稀释后的PCR 产物作为模板,进行20ul 体系的SYBR Green real-time PCR 反应,以检测管家基因(如GAPDH 、HPRT 、ACTB )的表达。 33、剩余未稀释的PCR 产物使用QIAquick PCR purification kit 进行纯化,并使用50ul EB buffer 进行洗脱; 34、-80℃ 储存。
29、每管中加入19ul PCR mix 2;
范文二:单细胞测序技术
单细胞测序——2013年最值得关注的测序技术
2013/01/31 生物探索
单细胞测序
| 全基因组测序 | 转录组测序
随着现代生物学的发展,细胞群体的研究已不再能满足科研需求。单细胞测序解决了用导
组织样本测序或样本少时无法解决的细胞异质性难题,为科学家研究解析单个细胞的行读
为、机制、与机体的关系等提供了新方向。单细胞测序已逐渐成为科研热点。
过去二十几年里,随着基因测序技术水平的提高以及千人基因组计划、癌症基因组计划、Meta-Hit计划等重大国际合作项目的相继开展,基因组研究日渐被推向高潮。然而,迄今为止使用的测序材料无一例外都是数百万甚至更多细胞的混合DNA样本。这种方法能够得到全基因组序列信息,但是对其进行研究得到的结果只是一群细胞中信号的平均值,或者只代表其中占优势数量的细胞信息,单个细胞独有的特性被忽视。例如,科学家想找出哪种突
变存在于哪种细胞中几乎是不可能的,只存在于少数细胞(如早期癌细胞)中的突变也基本上被掩藏。另一方面,有些样品稀少无法在实验室培养,样品量不足以进行全基因组分析,例如肿瘤循环细胞、组织微阵列、早期发育的胚胎细胞等。这些都是全基因组测序遇到的难题。
作为“在单个细胞水平上对基因组进行测序”的单细胞测序技术能够解决上述难题。与传统的全基因组测序相比,单细胞测序不仅测量基因表达水平更加精确,而且还能检测到微量的基因表达子或罕见非编码RNA,其优势是全方位和多层次的。
2011年,《自然方法》杂志( Nature Methods )将单细胞测序列为年度值得期待的技术之一[1],2013年,《科学》杂志(Science)将单细胞测序列为年度最值得关注的六大领域榜首[2]。与此同时,测序巨头相继推出新一代测序仪,为单细胞测序提供利器,越来越多与单细胞测序有关的研究也发表在顶级期刊上,这些都表明,单细胞测序已逐渐成为科研热点,有望成为2013年最值得关注的测序技术。
近年来,流式细胞分选和激光捕获显微切割技术的出现让单细胞的捕获成为可能。单细胞测序技术正逐渐从实验研究方法成为指导临床的有利工具,为基础研究向临床转化搭建了桥梁。单细胞测序主要涉及单细胞基因组测序和转录组测序两方面,分别针对单个细胞的DNA和RNA进行序列分析和比较,进而揭示基因组和转录组的变化。
单细胞全基因组测序
单细胞全基因组测序技术是在单细胞水平对全基因组进行扩增与测序的一项新技术。其原理是将分离的单个细胞的微量全基因组DNA进行扩增,获得高覆盖率的完整的基因组之后通过外显子捕获进而高通量测序用于揭示细胞群体差异和细胞进化关系。
全基因组扩增技术主要分为两种类型:一是基于热循环以PCR为基础的扩增技术,如简并寡核苷酸引物PCR (DOP-PCR)、连接反应介导的PCR (LM-PCR)、扩增前引物延伸反应 (PEP)等;一是基于等温反应不以PCR为基础的扩增技术,如多重置换扩增 (MDA) 和基于引物酶的全基因组扩增 (pWGA)。
在这两种类型中,PCR扩增比较经典,但是,对不同的序列来说,PCR扩增的效率存在相当大的偏差,易产生扩增偏倚问题: 如富含CG的DNA序列和相应基因座位的非随机丢失,等位基因的非随机丢失,以及与DNA片段大小相关的偏差(倾向于扩增更多短片段),尤其是在应用于单细胞时,大量短片段导致片段间序列丢失,从而使其应用受限。
MDA是目前公认的最好的单细胞基因组扩增技术,它能对全基因组进行高保真的均匀扩增,扩增出10~100kb大小的片段,能提供大量均一完整的全基因组序列。但是MDA也有一些缺点,特别是显著的非特异扩增,往往空白对照样品也总是“无中生有”地产生大量的DNA,另外就是仍然存在序列偏差。尽管各种改进的策略正在逐步减少这些缺陷,高覆盖率、高保真性及高特异性的扩增仍然是亟待解决的问题。另外,对测序得到 的大量数据结果的专业分析也是一个重大的挑战。 单细胞全基因组测序正在从基础研究走向临床应用。 单细胞转录组测序
单细胞转录组分析主要用于在全基因组范围内挖掘基因调节网络,尤其适用于存在高度异质性的干细胞及胚胎发育早期的细胞群体。与活细胞成像系统相结合,单细胞转录组分析更有
助于深入理解细胞分化、细胞重编程及转分化等过程及相关的基因调节网络。将此技术应用于临床,理论上可以在生理 或病理情况下连续追踪基因表达的动力学变化,从而监测疾病的进展。单细胞转录组分析的另一应用领域是发现亚细胞成分的基因表达谱,例如对在神经元的轴突或树突部分特异表达的基因的转录组的分析,这些基因往往对细胞的生物学功能发挥着重要作用。但是,鉴于目前的技术手段,单细胞转录组测序仍然存在覆盖率低的弊端,导致除mRNA以 外的长非编码RNAs难以检测,并且不能区分正义链与反义链。最近发展的单分子测序技术无需逆转录和扩增步骤而直接对单个细胞的全长mRNAs进 行测序,从而准确地检测基因不同的剪切亚型的表达水平。随着技术的发展这些局限性会被逐步优化和改进。
多重退火和成环循环扩增技术(Multiple Annealing and Looping-Based
Amplification Cycles, MALBAC)
主要研发人:哈佛大学终身教授、美国科学院院士谢晓亮(Sunney Xie)教授
技术看点:降低PCR扩增偏倚,使得单细胞中93%的基因组能够被测序。这种方法使得检测单细胞中较小的DNA序列变异变得更容易,因此能够发现个别细胞之间的遗传差异。这样的差异可以帮助解释癌症恶化的机制,生殖细胞形成机制,甚至是个别神经元的差异机制。 技术简介:
PCR扩增具有偏好型而且基因组具有大量的冗余,造成了基因组测序准确性不高。
谢晓亮研发的MALBAC技术能从一个细胞的基因组中,分离出来自单细胞的DNA,然后添加称作引物的短DNA分子。这些引物可与DNA的随意部分互补,从而使得它们能够附着到DNA链上,充当DNA复制起点。
这些引物由两个部分构成——一个包含8个核苷酸的粘性部分变化多样,可与DNA结合,再加上一个包含27个核苷酸的共同序列。这一共同序列可防止DNA太多次拷贝,大大地降低了扩增偏倚。通过将自身掺入到新拷贝链,从而自身成环,防止了过度拷贝。利用这种方法,进行与加入的引物的DNA复制时,可以完成高达93%的基因组测序。
技术论文:Genome-Wide Detection of Single-Nucleotide and Copy-Number Variations of a Single Human Cell
基于芯片实验室技术的单细胞测序
主要研发人:斯坦福大学Stephen Quake
技术看点:基于lab on a chip开发
技术简介:
本技术设计了一种路线,用液体载运细胞通过一连串显微管道和微阀门,当细胞挨个进入各自的小空位时,它们的DNA就会被提取出来,经过复制用于进一步分析。
此外,本技术不仅能分离细胞,还能用化学试剂将细胞混合起来,通过检测反应过程中的荧光发射获得它们的基因编码。所有这些都能在芯片上完成,不仅操作简单,而且成本效益高。
Stephen Quake已利用此技术完成了第一例人类单细胞测序,现在他正利用这项技术研究精子细胞中的重组并分析突变率。
技术论文:Genome-wide Single-Cell Analysis of Recombination Activity and De Novo Mutation Rates in Human Sperm
基于MDA的单细胞测序
主要研发人:深圳华大基因研究院
技术看点:将多重置换扩增(MDA)和测序技术相结合。
技术简介:
本技术基于多重置换扩增(MDA),并对该方法的扩增均一性、灵敏度、特异性等方面进行了全面评估。这种将多重置换扩增和测序技术相结合的单细胞测序方法不仅具有更高的分辨率和基因组覆盖度,而且具有更好的敏感性和特异性。该方法从单核苷酸水平上为各种复杂疾病和生物学过程的研究开辟了新思路。
技术论文:Single-Cell Exome Sequencing and Monoclonal Evolution of a
JAK2-Negative Myeloproliferative Neoplasm
Single-Cell Exome Sequencing Reveals Single-Nucleotide Mutation Characteristics of a Kidney Tumor
Strand-seq
主要研发人:加拿大英属哥伦比亚大学Peter Lansdorp
技术看点:能捕捉DNA一条链上的信息,使得研究人员能对亲本DNA模板链进行单细胞测序,避免单细胞DNA扩增和测序时丢失定向信息。
技术简介:
在细胞分裂过程中,当双螺旋解旋后,两条染色体上的遗传信息偶然会出现交换,如果这样的交换水平不断提高,就标志着出现了DNA损伤和癌症。传统的基因组测序,由于在单细胞DNA扩增和测序的时候,会丢失定向信息,难以检测到基因重排,因此也就检测不出这一点。
Strand-seq方法能分别对单细胞的双亲DNA模板链进行测序,获得高分辨率的姊妹染色体交换图谱,检测到基因重排,从而发现细胞复制过程中,DNA序列的翻转或交换。 利用Strand-seq方法,研究人员完成了单链DNA测序,并发现了首个基因组压力和不稳定性的痕迹。
技术论文:DNA template strand sequencing of single-cells maps genomic rearrangements at high resolution
单细胞测序解决了用组织样本测序时或样本少无法解决的细胞异质性难题,为从单核苷酸水平深入研究癌症发生、发展机制及其诊断、治疗提供了新的研究思路并开辟了新的研究方向。此外,这一新方法还可被广泛用于其他重要的生物研究领域,如组织器官内细胞基因组的异质性研究、干细胞的异质性研究、生殖细胞的遗传重组研究、胚胎的植入前遗传学诊断研究、法医学少量DNA测序等。
不过,就目前来说,单细胞测序最常见的应用是在癌症研究上。由于癌细胞中基因组部分被删除,或者扩增,从而引起关键基因的缺失,或者表达过量,干扰正常细胞生长,因此利用这种方法就能分析基因拷贝数目,从而诊断癌症。以下列出了单细胞测序常应用的领域。 肿瘤单细胞测序
已有的研究表明,基因或基因组变异是肿瘤发生的根本原因,利用单细胞全基因组测序技术,可以对获取的肿瘤细胞进行更为精确和深入的分析,发现正常细胞与肿瘤细胞差异,了解癌细胞的基因如何突变,以及肿瘤的来源、肿瘤的生长规律、属于哪种基因型等,为早期检测和诊断肿瘤和肿瘤的个体化治疗提供指导。另外,肿瘤的异质性是导致肿瘤耐药性问题的原因。如果 能从单个肿瘤细胞水平对肿瘤单细胞进行测序,并 找出一个肿瘤在单个细胞上的共同结构,揭露出每个肿瘤细胞的突变规律,这将为药物研究、肿瘤的靶向治疗提供基础。 2008年,美国华盛顿医学院的Ley等完成了对一位50多岁死于急性骨髓性白血病(acute myeloid leukemia, AML)的患者的基因组测序工作。他们利用高级流式细胞术分离出细胞表面CD13、CD33和CD117阳性,但CD34阴性的肿瘤细胞,并检测它的遗传突变。 最终在患者的肿瘤 DNA中仅发现了10个可能与AML有关的遗传突变, 其中8个很罕见,这也是首次发现的与AML有关的基因。通过单细胞分析技术,测得每个肿瘤样本细胞拥有9个突变[3]。
2011年,Navin等利用DOP全基因组扩增及DNA测序对单个乳腺癌细胞进行了拷贝数变异的分析,进而推断出细胞的群体结构和肿瘤的进化过程。但是由于该方法的基因覆盖率较低,而且不能在单个核苷酸的分辨率上评价单个肿瘤细胞的遗传学特征,故并不能检测在肿瘤发展过程中发挥重要作用的单个核苷酸的改变[4]。
2012年,华大基因首次利用以MDA为基础的单细胞测序技术对原发性血小板增多症
(essential thrombocythemia, ET)病人的单个骨髓细胞进行了测序并分析,筛查出在ET发病和进展中的驱动基因, 从而证实ET为单克隆来源的疾病[5]。同时,也将该方法与经典方法进行比较,从而建立了具有高敏感性、高特异性、假阳性率低等特点的单细胞测序方法,为分析疾病的遗传学结构特征及克 隆进化过程提供了新的思路。同样的方法也用于分析单个肾癌细胞的单核苷酸突变特征,从而在更高的分辨能力上为评价基因改变的复杂性提供了更为优化的方法[6]。
单生殖细胞测序
单细胞DNA扩增技术和高通量测序技术的发明,使得测序单个生殖细胞的基因组成为可能,利用单细胞全基因组测序技术来研究人类的染色体重组规律,具有以往技术无法比拟的优势。
美国科学院院士、哈佛大学教授谢晓亮课题组与北京大学生物动态光学成像中心(BIOPIC)研究员李瑞强课题组联合起来,将单细胞测序应用到一个单一的亚洲男性精子的DNA测序,结果发现基因区附近重组率的降低由分子机制所决定,而非自然选择的结果,证明这种方法能准确识别单个核苷酸的变化。这项工作首次实现了高覆盖度的单个精子全基因组测序,构建了迄今为止重组定位精度最高的个人遗传图谱,这一技术方法在男性不育症研究和肿瘤早期诊断及个体化治疗等生物医学领域有着广泛的应用前景[7]。
美国斯坦福大学医学中心的研究人员借助单细胞测序技术对源自一名男性的91个精子细胞的全部基因组进行了测序,发现许多新的重组热点和与间接方法发现的相一致的比率。 随
后他更深程度地测序了8个精子足以确定突变率。这将有助于学界更加了解自然发生的个体遗传突变,对于不孕不育症的科研具有重要意义[8]。
美国艾伯特爱因斯坦医学院的统计遗传学家Auton在2012年冷泉港的基因组生物学会议上报告说,对近200个精子细胞进行的测序,能够估算出捐精给他们的男子的重组率。该研究工作详细结果还未发布,Auton仅表示,他们发现每个精子细胞平均有24.5个重组事件,与来自间接实验的结果相一致。
微生物单细胞测序
人体内和环境中生存着各种微生物,但大部分微生物不能在实验室中培养,这阻碍了研究人员对它们的测序和研究。单细胞测序能够用来深入研究单个细菌细胞的基因组。
来自J. Craig Venter研究所、加利福尼亚大学以及Illumina Cambridge公司的研究人员就尝试着对加利福尼亚海洋样本中的单个细菌——SAR324细胞基因组进行了测序。
研究人员使用的单细胞测序方法利用了多次替换扩增、Illumina GAIIx末端配对测序,以及一种新的能够解决扩增偏向的单细胞装配算法(EULER+Velvet-SC)。他们在大肠杆菌和金黄色葡萄球菌上验证可行性后,随后将研究对象换成SAR324,结果生成了单细胞基因组序列,装配出430万个碱基的contig序列,其中含有3811个开放阅读框,获得了传统全基因组研究中缺少的细胞特异的遗传信息。
尽管还需要进一步研究来弄清SAR324在环境中的作用,但基因组模式表明该细菌是好氧菌,且移动的。结合tRNA、氨基酸和维生素相关基因,研究人员还发现了参与有氧代谢、鞭毛形成及趋化作用的基因。
今后,研究人员计划使用相似的策略对不同环境中的单个细菌细胞进行测序,从大海深处到医院病房及人体内。作者认为,这种经济高效的方法应该有助于微生物分类和进化的探索,且能够挖掘出一些环境微生物,其基因和通路能够为生物技术和生物医学所用[9]。
从2011年到2012年,经过了两年迅速的技术演进,单细胞测序吸引了众多研究人员的眼球,但是它还没有取得质的飞跃,仍然处于不成熟的阶段,在技术上和成本上还远没有达到大规模应用的地步。
但是,单细胞测序的前景依然是乐观的。美国马里兰州贝塞斯达美国国家人类基因组研究院(National Human Genome Research Institute in Bethesda, Maryland)的遗传学家Elaine Ostrander说:单细胞基因组测序技术是一种让人难以置信的新技术,这种技术的应用潜力无法估量,我们可以凭借这种技术轻而易举的攻克肿瘤难题。
中国华大基因研究院副院长李英睿说:“单细胞测序新方法为遗传异质性肿瘤的高精度、全面评估提供了一个非常优秀的研究工具。这种新方法和产生的数据为鉴定与肿瘤发展相关的候选基因提供了科学依据,也必将会推动癌症的遗传机理和生物学过程更深入的研究。” 我们有理由相信,在不远的未来,单细胞测序将会把组织器官内细胞基因组的异质性研究、干细胞的异质性研究、生殖细胞的遗传重组研究、胚胎的植入前遗传学诊断研究等领域带入一个前所未有的精致程度,我们将迎来更多革命性的科技进步。
[1]Single-cell methods
[2]Single-Cell Sequencing Tackles Basic and Biomedical Questions
[3]DNA sequencing of a cytogenetically normal acute myeloid leukaemia genome
[4]Tumour evolution inferred by single-cell sequencing
[5]Single-Cell Exome Sequencing and Monoclonal Evolution of a JAK2-Negative Myeloproliferative Neoplasm
[6]Single-Cell Exome Sequencing Reveals Single-Nucleotide Mutation
Characteristics of a Kidney Tumor
[7]Probing Meiotic Recombination and Aneuploidy of Single Sperm Cells by Whole-Genome Sequencing
[8]Genome-wide Single-Cell Analysis of Recombination Activity and De Novo Mutation Rates in Human Sperm
[9]Ubiquitous dissolved inorganic carbon assimilation by marine bacteria in the Pacific Northwest coastal ocean as determined by stable isotope probing
范文三:单细胞分析
山东大学 博士学位论文 单细胞分析 姓名:翁前锋 申请学位级别:博士 专业:分析化学 指导教师:金文睿 2001.10.10
山东大学博士学位论文 第一章单细胞的毛细管电泳分析 ^
图1-5单个细胞细胞质进样电泳及毛细管进样端蚀刻示意图
1.2.2检测技术
由于单细胞内组分的含量非常少,一般在fmol至zmol的范围内,这就 要求CE的检测器至少能达到fmol级检测限,因此检测器是建立单细胞CE 分析方法的关键.CE检测器种类很多,但用于单细胞多组分分离和定量检测 的主要有电化学检测器和激光诱导荧光检测器(LIF),其次,紫外检测【32】, 放射化学检测[14】,质谱检测【33],在柱微型免疫分析[34】也已有报道。 1.2.2.1电化学法
毛细管电泳电化学检测(CE.ECD)包括电导法检测、电势法检测和安 培法检测三种模式『35]。目前安培法检测可用于单细胞分析。扫描伏安法检 测器应用于单细胞分析也有报道f36]。安培检测器需解决的首要问题是克服 高压电场对微电极检测的影响。一般认为,当毛细管内径小于或等于25gm 时,可将微电极置于末端管口直接构成柱端安培法检测器【37],但当毛细管 内径超过25tun时,分离高压产生的基线噪音和漂移较明显,为此,已有多 种接口被用于排除高压电场对微电流检测的干扰【38-40].
安培检测模式原理就是在三电极体系中,在工作电极加一恒定电势,当 待分析物从分离毛细管流出后在电极上发生电子转移反应,记录此时的电流 信号,得电流.时间曲线(流出曲线).扫描伏安法检测器是在工作电极上加 “9
r 山东大学博士学位论文 第一章_.细胞的毛细管电泳分析
一快速线性递增的电势并记录电流信号。当待测物流出时,可以记录下特征 伏安曲线。不同的物质有不同的伏安哇毪线。因此它可以帮助我们对流出时间 相近的物质进行定性。电化学检测的局限在于只能检测易氧化还原的物质. Ewing研究小组【27】首先将毛细管电泳安培检测用于单细胞分析,并进 行过系统的研究工作.他们利用CZE离柱式安培法首次检测了池塘蜗牛神经 细胞(直径200tun)的细胞质。采用10gm碳纤维电极和内径12.7tun的毛 细管柱,用多孔玻璃做接口隔绝分离电压的影响,通过一微进样器移取蜗牛 神经细胞的细胞质进样,电泳分离后用恒电势安培检测。但当时不能证实各 电泳峰的成分.从此以后,CZE/安培检测用于单细胞分析发展很快。
当Ewing等【4l】采用全细胞进样cE安培检测分析单个只Comeus多巴 胺神经细胞时,发现溶解细胞的时间变短会造成迁移时间不同的两个多巴胺 峰,当细胞培养液中加入利血平(一种泡囊破坏荆)培育一段时间后再单细 胞进样,则只有一个多巴胺峰。据此推断他们是来自不同的贮存多巴胺的泡 囊。为证实上述推测,Ewing小组[36】将毛细管电泳与扫描伏安法检测相结 合用于上述多巴胺神经细胞的分析。图1-6A是实验得到的单个多巴胺神经 细胞在细胞溶解时间较短时(1rain)的三维电泳图。图1-6B是图1-6A中 将背景扣除后从峰A和峰B中提出的电流值所组成的伏安图,由图1-6B可 判断峰A和峰B都是多巴胺的峰。显然,扫描伏安检测与毛细管电泳结合可 为胞内物质的定性提供更多的信息。
1.2.2.2激光诱导荧光法
激光诱导荧光(LⅡ)检测是通过将激光光束在毛细管内聚焦成很小的 光斑作为检测窗口实现的.LIF具有很高的灵敏度,检出限已达到分子水平 ymol(10-24t001),并已用于检测单个乳酸脱氢酶分子【42】和单个藻红索分子 【43】.但通常其检出限在amol~zmol范围内。CE与激光诱导荧光检测相结 合,兼有高分辨和高灵敏度的特点.波长分辨激光诱导荧光法可以同时检测 分析物区带的荧光发射光谱,因而可以对迁移时间相近的谱带具有定性的能 力【44】.
山东大学博士学位论文 第一章单细胞的毛细瞥电泳分析
图1-6三维电泳图(1-6A):峰人B背景扣除后的伏安图(1—6B)
激光诱导荧光法又可分为天然荧光法,化学标记荧光法,间接荧光法和 催化荧光法。激光诱导荧光法可以直接应用于具有天然荧光的物质。具有天 然荧光的物质主要包括一些蛋白质和儿茶酚胺类物质。然而,具有天然荧光 的物质毕竟是少数。对于那些我们感兴趣又具有可标记基团的物质,可以采 用化学标记荧光法。即通过化学反应标记上荧光基团,然后电泳分离检测。 因此一系列的荧光衍生试剂随之发展起来。荧光试剂有萘.2,3.二羧醛 (NDA),邻苯二甲醛(OPA),3-(4.羧基甲酰基).2.奎宁羰醛(CBQCA)以及 荧光胺,可以用来标记氨基酸、蛋白质、肽和碳水化合物等。上述荧光试剂 具有独特的优点,它们或者自身无荧光而标记产物有荧光,或者衍生产物的 水解产物不具荧光特性.另外,针对含巯基基团物质的衍生试剂有荧光索和 mBBr,但这两种试剂自身也具有荧光信号。其它荧光试剂还有丹磺酰氯 (DANsYL)及荧光索异硫氟酸盐(FITC)等.
对于一些既无天然荧光又难以被荧光试剂标记的物质则可以采用间接荧 光检测.在电泳缓冲液中加入一定量的荧光试剂。当非荧光的分析物流经检 测窗口时,因荧光信号的减弱会产生一个倒峰.倒峰的大小与分析物的浓度
有着定量关系.
山东大学博士学位论文 第一章单细胞的毛细管电泳分析
催化荧光检测本质上也是一种间接检测方法。它不是直接测定被分析物, 而是通过测定待分析物与其它物质反应后产生的具有荧光信号的物质,来定 量待分析物的一种方法,Xue等[45】最早将毛细管电泳催化荧光检测法应 用于单个人血红细胞中乳酸脱氢酶(LDH)活性分析。乳酸与烟酰胺腺嘌呤 二核苷酸(NAD+)在单细胞胞内LDH催化下,生成NADH,检测NADH 的荧光强度,可以测得单个人血红细胞中乳酸脱氢酶同工酶的活性。检测限 达1.3X 10m tool(约800个分子)。他们的研究说明单个人红血球细胞LDH 平均活性为1.36±0.7nIU.单个细胞之间LDH的活性差异大,衰老红细胞 的酶活性较低。
1.2.2.3在柱微型免疫检测
Rosenzweig等【34】提出一种CE的在柱微型免疫检测方法,电泳毛细管 内填充与抗体共价键合的胶体颗粒,在高压电场的作用下胶体颗粒发生迁移, 利用抗原分子与抗体专一性结合作用和激光光散射检测反应颗粒的个数,可 测定不同红细胞中葡萄糖矗磷酸脱氢酶(G6PDH)的含量,检铡限达1zmol (约620个分子)。测得人单个红血球细胞中G6PDH的平均含量为34zmol。 Tan和Yeung【46】还设计组装了经毛细管电泳分离后,用粒子计数免疫检测 法测G6PDH的含量,激光荧光法测G6PDH活性的装置,可同时测定人单个 红细胞中G6PDH的量和活性。红血球细胞分析结果,每个细胞中G6PDH平 均含量为15±9zmol;活性27±14pIU。
1.2.2.4放射法
Sweedler研究组【47】报道了一种柱后放射性检测装置,用”s,32P或3H 标记蛋氨酸,经毛细管电泳分离,设计的柱后分布收集装置将毛细管流出液 分布收集在可键合肽的膜上,膜收集器可双向移动。用CCD检测器阵列检测 斑点,获得电泳谱图.该方法灵敏度高,35S标记分析法的检出限为17amol, 检测了海软体动物(加州Aplysia)单个脑神经细胞Bl中的神经肽[14】。
范文四:单细胞凝胶电泳技术影响因素的分析
单细胞凝胶电泳技术影响因素的分析
7破
单细胞凝胶电泳技术影响因素的分析?
马爱国臧金/刘四朝
单细胞凝胶电泳(SCGE)又称"彗星"法,是一种 操作简便,快速,敏感性高的DNA损伤与修复的检 测技术_1J.尽管此法无需复杂的实验条件,但在建 立过程中可能受诸多因素的影响而难以得到较理想 的结果,我们就其主要的影响因素作如下分析. 1.琼脂糖凝胶薄板的制备:该实验需要制备两 层琼脂糖凝胶薄板,应注意琼脂糖的浓度,制备时
第1层是紧贴冰冻玻片砂面的1%正常 间和温度.
凝点(42?2)?的琼脂糖凝胶,吸取85制成面积 为l8rr?I×l8mm.厚度为0.2.5rr?I的凝胶.然后置 4~C存放约?分钟,如时间过短,不能得到"老化" 的凝胶与玻片粘合不紧,容易在液体浸泡处理和电 泳过程中自然脱落,造成实验失败;反之,如果放置 时间过长,凝胶极易干裂而脱落.第2层凝胶是 1%低凝点(26?2)?琼脂糖液,与细胞混合时琼脂 糖液的温度30—37?,温度过高可引起细胞损伤, 此操作过程力求快速,以免加速细胞DNA的修复. 2.细胞数和实验温度的影响:
(1)实验细胞数应调至约3.0×lo5,如果细胞数 过低,一张片子中细胞数太少,很难完成100个彗星 计数分析;反之细胞数过高,片中细胞过密,位于不 同层面的细胞相互重叠,难以分析彗星DNA损伤. (2)实验温度的控制.样品应置4?环境下进
行,以抑制或降低核酸内切酶等活性,阻止DNA损 伤的修复,从而达到准确地检测DNA初级损伤.已 有研究表明一些细胞DNA断裂损伤能在1小时内 达到90%的修复,3小时达到97%E,因此,应严格 控制细胞在分析过程中的温度.
3.碱化处理及电泳的条件:凝胶内的细胞需在 碱性(pH值1O)环境下进行处理,其作用一是去除 细胞蛋白质,使DNA暴露出来;其次是碱化处理使 DNA紧密螺旋结构解旋,DNA损伤片断及其极性端 暴露出来t.
作者单位:266021青岛大学医学院医学营养学系(马爱国,藏金 林);中国农业科学院研究生院(刘四朝)
取j
.
实验研究.
电泳条件:电压或电流过大,严重受损伤的细胞 可能出现的拖尾过长,彗星消失而影响结果,其次 是正常的细胞可能因电压或电流过大而形成少许拖 尾的假阳性结果.反之,电压或电流过小,受损伤的 细胞不会出现拖尾,而出现假阴性结果.电泳的电 压多选用低电压,一般在l8—50v,在电泳过程中电 泳液的温度应不超过15?(应在4?条件下进行), 电泳时间多在20—40分钟.
4.荧光染色及彗星图象分析:
(1)采用DAPI荧光剂染色,质量浓度在1—5 舀/,用量为1O.染色15分钟后即可观察,视野 中明亮荧光的"彗星"被光照时间一般不易超过2分 钟,以免荧光剂快速衰退而不宜继续观察和拍照. (2)彗星的图像分析主要靠肉眼显微镜读片,
对DNA损伤程度标准的正确判断是非常重要的. 不同程度损伤可根据彗星的尾部与其头部的比率大 小分为0,1,2.3,4五个等级.0级无拖尾表明无损
伤,当DNA损伤程度由轻到重,则彗星的尾部逐渐 变长变大,头部逐渐变小荧光强度逐渐变弱.用肉
眼观察判断的分级需要通过计算机彗星图象分析加 以确定,目前已有彗星电脑分析软件可供使用,如
Komet3.0等…4.总之,严格控制SCGE的各种影响 因素,使其真正成为一种可靠,易于掌握和有效的
DNA断裂损伤和修复检测的新技术J.
参考文献
1马爱国,韩秀曩.剂四朝.等.两种DNA断裂搁伤检测方法敏感 性比较遗传.1997.19:32.34
2马爱国,Cdlir.sAR,l~[hiesJ,等不同细胞DNA氧化捆伤及自 身修复能力的分析癌变畸变突变.1997,9:138.142 3sJrCdlir.sAR,C.G,Ha1QIH喊andr町pro-
tect唁血由衄pem~de.-iMueMDNAd'劬舢dkBand oxidisedpyrimidine*)inhumanb?Murat,1997r393: 翌3.23I
4CollimAR.InVL.DmindmM,d.11.ecometamay:what锄 itreallyte?Ufl?Murat.1997.375:183.193 5CollimARrDmindmMrFranklinM,d0脚dA邺inhtmma bmq山Dg曲j?{eIi血可.Iid吐,and衄t_舢.EnvMm MMMutagen.1997.30:139-146. (收稿:1998~X5-29謦回:1998.12-17) (本文编辑:荆群)
范文五:单细胞藻类培养技术
实用技术—生物饵料责任编辑 李振龙
单细胞藻类培养技术
◇田程 崔建升 刘杰河北科技大学环境科学与工程学院 050018
单细胞藻中含有大量的多聚不饱和脂肪酸
(PUFAs)、EPA和DHA,而且多数的单细胞源的二级培养接种比例为1∶10,以二级培养为种源的扩种比例为1∶5。扩种一般选在上午8∶00到10∶00进行。
当二级培养的藻种经5天~6天培养后,临近对数生长期时,可进行生产性扩种。扩种比例为1∶40左右,扩种时间一般在上午9∶00到10∶00。藻具有生长繁殖快、环境适应力强、培养周期短等特点。可实现在人工控制条件下大量培养获得高产的目的,是鱼、虾、贝类等海产品的理想鲜活饵料,藻类培养质量的
好坏将直接影响海产品育苗的成败,因此单细胞藻类的培养技术是育苗成功的基础和关键技术。随着人工育苗技术的成熟,单细胞藻类在贝类、虾蟹类、鱼类人工育苗中得到了广泛应用。以下简述一下藻类培养的注意问题:三、管理藻类培养过程中光照、温度、湿度等条件的控制对藻类生长都起到十分关键的作用,因此接种后加强培养池的管理是提高产量的重要环节。生产性培养要用网捞出池面的
污物,保持池水的洁净;为使藻处于悬浮的状态,不沉入池底,使其进行光合、呼吸作用且营养分布均匀,每天搅拌池水6次~8次;一级培养也要每天人工摇动3次~4次,以使藻类生长均匀,防止藻类出现沉淀与附壁现象。
1.对藻类生长状况的日常检查
每天早晚各做一次全面检查,观察藻类的颜色、透明度、附壁、沉淀和充气状况,必要时可配合显微镜检查。扩种后的藻种颜色很明显的由浅变深,若颜色变化不明显或出现其他颜色转变,就要及时查找原因;藻类对生长环境变化敏感,当出现环境不适应时就会出现沉淀和附壁现象;藻种一旦出现浑浊现象一般就要考虑是否存在敌害生物的污染,基于以上每天对藻种做日常检查是十分必要的。
2.镜检
显微镜检查是藻类培养中不可缺少的一步,一般7天~10天需进行一次全面的镜检,主要目的是检查有无敌害生物的污染,鉴定敌害生物的种类,从而及早采取相应措施。当培养出现异常现象时应及时镜检。
3.培养条件控制
不同的单细胞藻类品种有不同的生长最适温度,培养温度的高低直接影响其繁殖速度。过大的温差对单胞藻培养是十分不利的,尤其是在冬季,在向培养池补充水分或接种时,应尽量将水温调至所培养藻种的适温范围之内。当培养水温达到29℃以上时,对藻类生长不利,藻体老化快、易污染。在夏季控温的最好办法是将门窗打开,通风降温。
光照是影响单胞藻生长的主要因素之一。夏季,不要把藻类培养物放在直射太阳光下,而要放在凉爽的场所。在秋、冬季节,如希望藻类保持积极的生活活动状态,就要把培养物移到有人工光照处。而生产性培养、规模化培养需要较强的光照,可以人工补充光源强度。一、培养方式根据藻种培养的目的和要求的不同,单细胞藻的培养方式也有多种。根据藻的纯度一般分为纯种培养和单种培养。培养方法主要分为保种室培养和生产性培养。目前水产养殖过程中最为基础的培养是直接在自然水域中培养单细胞藻。经过滤的海水或淡水里有硅藻、绿藻等各种单细胞藻;有轮虫、桡足类、枝角类等各种浮游动物;有多种小型底栖动物等,利用繁殖自然水体里本身就有的单细胞藻,促进浮游动物、底栖动物等基础饵料生物的生长繁殖。而随着土池育苗的发展以及藻类在毒理学科研的需要,也可使用封闭或半封闭方式定向培养纯种单细胞藻。二、扩种目前的生产性培养主要分为一级、二级和三级培养。一级是藻种活化培养,一般在单细胞藻的保种室里进行,多采用250mL~5000mL的三角烧瓶,逐渐扩大培养;二级是藻种扩大培养,采用40L或50L的塑料桶、塑料袋充气培养单细胞藻;三级是在土池里投喂饵料的培养。刚买回来的藻种一般进行一级扩种,扩种过程要求严格的无菌环境,最好每天早上7∶30左右,时间不易过早,待藻种上浮后扩种,取上层活跃藻体转接。不宜在晚上接种,因为晚上不少藻类沉在底部,而白天藻类进行光合作用,趋光上浮,便于观察其运动能力,还可起到选种的作用;刚买回的藻种第一次转接时不易全部转接,转接其三分之一至二分之一即可,并放在温度较低、光线较弱的地方培养,待藻适应光照条件后再调至其生长所需正常温度、光照条件进行培养,20天左右转接一次。陈爱华等对等鞭金藻培养密度和接种时间比较试验结果表明,接种密度越低,生长速度越快,生长倍率越高。接种比率也是在藻种培养中需要注意的问题:以一级培养为种
《中国水产》2011年第5期



 山蛋蛋类那个红艳艳艳
山蛋蛋类那个红艳艳艳